L’Analyse de Variance (ANOVA) expliquée par le code
De l’import du fichier Excel à la conclusion automatisée — chaque ligne du script Python décryptée, chaque test statistique illustré.
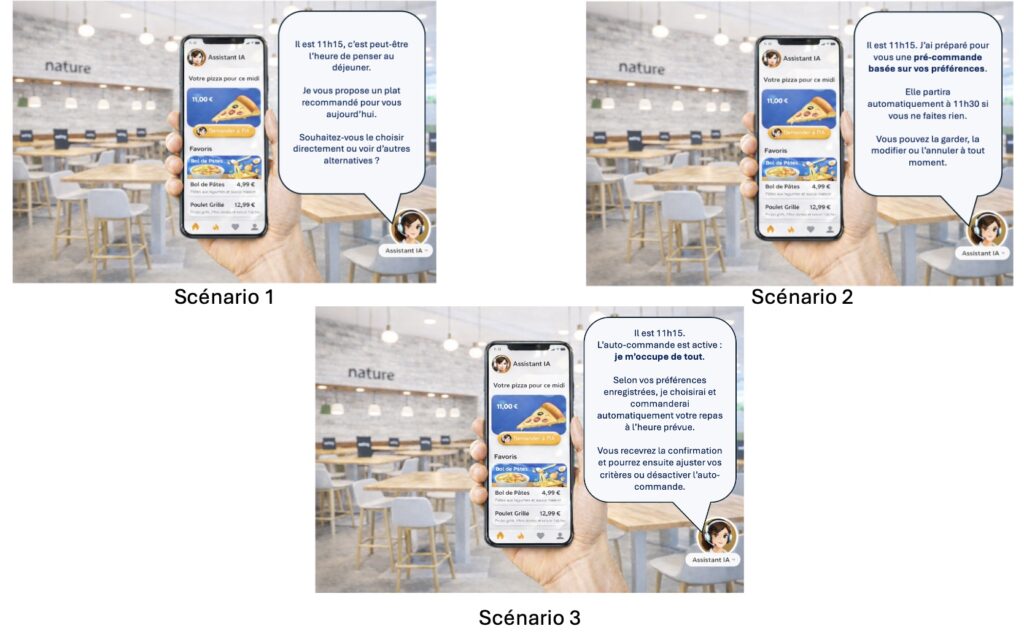
L’objectif de cette méthode : Dans notre étude, nous avons testé 3 scénarios différents impliquant un agent d’Intelligence Artificielle (IA) chargé de commander des repas à la cantine. L’ANOVA est l’outil statistique qui permet de savoir si la perception des utilisateurs change réellement d’un scénario à l’autre, ou si les écarts de notes (sur l’échelle de 1 à 5) sont simplement dus au hasard des profils interrogés
- Chargement & recodage des données
- Analyse en Composantes Principales (ACP)
- Statistiques descriptives
- Test de Levene (homogénéité)
- Table ANOVA & test de Welch
- Tailles d’effet (η² et ω²)
- Comparaisons post-hoc (Tukey)
- Double boucle & synthèse finale
🔍 Les 4 dimensions mesurées (variables dépendantes)
Chaque participant évalue l’agent sur ces 4 construits, mesurés via plusieurs items sur une échelle de Likert (1 à 5) :
- Alignement (5 items) — L’agent agit-il dans mon intérêt ou celui du restaurant ?
- Compétence (4 items) — L’agent fait-il de bonnes suggestions de repas ?
- Contrôle (5 items, dont 1 inversé) — Est-ce que je garde la main sur la commande ?
- Intention d’usage (4 items) — Suis-je prêt(e) à utiliser ce mode à l’avenir ?
La variable indépendante (facteur) est le numéro de scénario, stocké dans la colonne GROUPE (valeurs 1, 2 ou 3).
Vue d’ensemble du pipeline
Chaque nœud correspond à une section précise du code Python.
Chargement et préparation des données
Le socle de toute analyse : importer, filtrer et recoder.
Le script lit le fichier RC_AGENT.xlsx (feuille BASE), puis ne conserve que les lignes où GROUPE vaut 1, 2 ou 3 — ce qui exclut d’éventuels pré-tests ou données incomplètes.
import pandas as pd import numpy as np file_path = '/content/RC_AGENT.xlsx' df = pd.read_excel(file_path, sheet_name='BASE') # Filtrage : on ne garde que les 3 groupes expérimentaux df_analysis = df[df['GROUPE'].isin([1, 2, 3])].copy()
L’item CTRL3R_S1 est formulé de façon négative (ex : « J’ai le sentiment de ne PAS avoir le contrôle »). Un score élevé (5/5) y signifie en réalité un faible contrôle perçu. Le code inverse donc l’échelle : 1↔5, 2↔4, 3 reste 3. Après recodage, un score élevé signifie toujours « plus de contrôle », comme pour les autres items du construit.
# Inversion de l'échelle : 1↔5, 2↔4, 3=3 mapping_inverse = {1: 5, 2: 4, 3: 3, 4: 2, 5: 1} df_analysis['CTRL3R_S1'] = df_analysis['CTRL3R_S1'].map(mapping_inverse)
Le dictionnaire Python concepts regroupe les colonnes du questionnaire par dimension. Ce mapping sera utilisé à l’étape suivante (ACP) pour fabriquer un score unique par construit.
| Construit | Items du questionnaire | Nb |
|---|---|---|
| Alignement | ALIGN1_S1 … ALIGN5_S1 | 5 |
| Compétence | COMP1_S1 … COMP4_S1 | 4 |
| Contrôle | CTRL1_S1, CTRL2_S1, CTRL3R_S1, CTRL4_S1, CTRL5_S1 | 5 |
| Intention | INT1_S1 … INT4_S1 | 4 |
Le dictionnaire item_labels fournit en parallèle un libellé lisible pour chaque code (ex : COMP2_S1 → « Fait de bonnes suggestions de repas »). Ces libellés apparaîtront dans les sorties console et les graphiques.
Étape préliminaire — l’ACP
Résumer plusieurs questions en un score unique et robuste.
On pourrait calculer la moyenne brute des 5 items d’Alignement. Mais l’Analyse en Composantes Principales (ACP) fait mieux : elle attribue un poids différent à chaque item selon sa contribution réelle à la dimension commune. Un item qui « colle » parfaitement au concept pèsera plus lourd qu’un item un peu périphérique. Le résultat est un score standardisé (centré-réduit) par participant, plus fiable statistiquement qu’une simple moyenne.
Cliquez ici pour en savoir plusLe code enchaîne trois opérations pour chaque construit :
from sklearn.decomposition import PCA from sklearn.preprocessing import StandardScaler pca_df = pd.DataFrame({'GROUPE': df_analysis['GROUPE']}) for name, items in concepts.items(): # 1. Standardisation : moyenne → 0, écart-type → 1 scaler = StandardScaler() # 2. Extraction de la 1ère composante principale pca = PCA(n_components=1) # 3. Projection : score unique par participant pca_df[name] = pca.fit_transform( scaler.fit_transform( df_analysis[items].fillna(df_analysis[items].mean()) ) ).flatten()
Détail des 3 opérations internes :
1. StandardScaler() — Chaque item est centré (moyenne ramenée à 0) et réduit (écart-type ramené à 1). Cela empêche un item dont les notes sont naturellement plus élevées ou plus dispersées de dominer le score final.
2. PCA(n_components=1) — On ne retient que la première composante, c’est-à-dire la direction de variance commune maximale entre les items. L’ACP trouve la combinaison linéaire qui explique le plus de variabilité : plus un item « va dans le même sens » que les autres, plus son poids (loading) sera élevé.
3. fillna(mean()) — Si un participant n’a pas répondu à une question, sa valeur manquante est remplacée par la moyenne de cet item pour ne pas perdre l’ensemble de ses données.
Les 5 étapes de l’ANOVA
Chaque étape est exécutée automatiquement par la fonction run_full_analysis() pour chaque variable testée.
Premier réflexe du chercheur : regarder les chiffres bruts. Le code calcule la moyenne, l’écart-type, la variance et l’effectif de chaque groupe, puis identifie automatiquement quel scénario obtient la meilleure et la plus faible note.
# Tableau récapitulatif par groupe desc = data.groupby('GROUPE')[target].agg( ['mean', 'std', 'count', 'var'] ).round(3) # Identification automatique du meilleur / pire scénario max_g = desc['mean'].idxmax() min_g = desc['mean'].idxmin()
La méthode .agg() applique quatre fonctions d’agrégation à chaque groupe en un seul appel. Le code repère ensuite le meilleur et le pire scénario pour générer une phrase d’interprétation automatique.
Mais attention : un écart de moyennes ne prouve rien à lui seul. Si le Scénario 1 obtient 3,9 et le Scénario 3 obtient 3,6, cette différence de 0,3 point pourrait n’être que du bruit statistique. Les étapes suivantes vont le vérifier.
L’ANOVA classique repose sur une hypothèse technique : les trois groupes doivent avoir des variances à peu près égales. Le test de Levene vérifie cette condition. S’il la rejette, le résultat de l’ANOVA classique pourrait être faussé.
from scipy import stats # Séparation des scores par groupe g1 = data[data['GROUPE']==1][target] g2 = data[data['GROUPE']==2][target] g3 = data[data['GROUPE']==3][target] # Test d'homogénéité des variances levene_stat, levene_p = stats.levene(g1, g2, g3)
La fonction stats.levene() de SciPy compare la déviation médiane des observations dans chaque groupe et renvoie une statistique F accompagnée de sa p-value :
Les variances sont homogènes. L’ANOVA classique est fiable.
Un groupe est plus dispersé. Le code bascule vers le test de Welch (étape 3b).
L’ANOVA décompose la variation totale des scores en deux sources :
Variation inter-groupes (SSbetween) — la part de variation expliquée par le changement de scénario. Plus les moyennes des 3 groupes divergent, plus cette valeur est grande.
Variation intra-groupe (SSwithin) — la part « résiduelle » due aux différences individuelles. C’est le bruit naturel.
from statsmodels.formula.api import ols from statsmodels.stats.anova import anova_lm # Modèle linéaire : score expliqué par le facteur GROUPE model = ols(f"{target} ~ C(GROUPE)", data=data).fit() anova_tab = anova_lm(model, typ=2) # Extraction des composantes de la table ss_bet = anova_tab.loc['C(GROUPE)', 'sum_sq'] # SS inter-groupes ss_err = anova_tab.loc['Residual', 'sum_sq'] # SS intra-groupe df_bet = anova_tab.loc['C(GROUPE)', 'df'] # ddl inter (k-1 = 2) df_err = anova_tab.loc['Residual', 'df'] # ddl intra (N-k) ms_bet = ss_bet / df_bet # Moyenne des carrés inter ms_err = ss_err / df_err # Moyenne des carrés intra f_stat = anova_tab.loc['C(GROUPE)', 'F'] p_val = anova_tab.loc['C(GROUPE)', 'PR(>F)']
La syntaxe C(GROUPE) indique à Python de traiter GROUPE comme une variable catégorielle : les valeurs 1, 2, 3 sont des étiquettes, pas des grandeurs numériques. Le paramètre typ=2 demande une ANOVA de type II — avec un seul facteur, les types I, II et III donnent les mêmes résultats.
La table produite ressemble à ce qu’afficherait SPSS :
| Source | SS | df | MS | F | Sig. |
|---|---|---|---|---|---|
| Inter-groupes | SSbet | 2 | MSbet | F | p |
| Intra-groupe (Résiduel) | SSerr | N − 3 | MSerr | — | — |
Moins de 5 % de chance que les écarts soient dus au hasard.
Les 3 scénarios génèrent la même perception.
Si Levene a déclenché une alerte (p < 0,05), le code bascule sur le test de Welch. Ce test pondère chaque groupe par l’inverse de sa variance : les groupes consensuels pèsent davantage, corrigeant le biais.
def welch_anova_test(data, target, group_col='GROUPE'): k = data[group_col].nunique() # Nombre de groupes (3) n = data.groupby(group_col)[target].count() means = data.groupby(group_col)[target].mean() vars_ = data.groupby(group_col)[target].var(ddof=1) # Poids = effectif / variance → groupes consensuels pèsent plus weights = n / vars_ sum_weights = weights.sum() grand_mean_welch = (weights * means).sum() / sum_weights # Statistique F de Welch num = (weights * (means - grand_mean_welch)**2).sum() / (k - 1) lam = ((1 - weights / sum_weights)**2 / (n - 1)).sum() den = 1 + (2 * (k - 2) / (k**2 - 1)) * lam f_welch = num / den df1 = k - 1 # Degrés de liberté ajustés (souvent non entiers) df2 = (k**2 - 1) / (3 * lam) p_val = stats.f.sf(f_welch, df1, df2) return f_welch, p_val
Points clés :
— weights = n / vars_ : poids élevé pour les groupes homogènes, faible pour les groupes très dispersés.
— grand_mean_welch : grande moyenne recalculée avec ces pondérations.
— df2 : degrés de liberté ajustés par Welch-Satterthwaite, généralement non entiers (ex : 45,7), rendant le test plus conservateur.
Une p-value < 0,05 certifie l’existence d’un effet mais n’en mesure pas la force. Avec un très grand échantillon, même un écart infime devient significatif. Les tailles d’effet quantifient la puissance pratique.
def calculate_eta_omega(ss_bet, ss_err, df_bet, ms_err): ss_tot = ss_bet + ss_err # η² — proportion brute de variance expliquée eta2 = ss_bet / ss_tot # ω² — estimation corrigée (moins biaisée) omega2 = (ss_bet - (df_bet * ms_err)) / (ss_tot + ms_err) return eta2, omega2
η² (Eta-carré) est intuitif mais surestime l’effet. ω² (Omega-carré) corrige ce biais en retirant la part de hasard attendue (df_bet × ms_err). Si ω² tombe sous zéro, max(0, omega2) le force à 0.
Effet faible
Effet modéré
Effet fort
L’ANOVA dit « au moins un groupe diffère ». Le test de Tukey HSD compare chaque paire en contrôlant le risque d’erreurs multiples. Avec 3 groupes : 1 vs 2, 1 vs 3, 2 vs 3.
from statsmodels.stats.multicomp import pairwise_tukeyhsd # Uniquement si l'ANOVA (ou Welch) est significative if reported_p < 0.05: tukey = pairwise_tukeyhsd(data[target], data['GROUPE']) print(tukey) else: print("Non nécessaire.")
Lecture de la sortie :
| Colonne | Signification |
|---|---|
group1 / group2 | Les deux scénarios comparés |
meandiff | Différence des moyennes (group2 − group1) |
p-adj | p-value ajustée pour comparaisons multiples |
lower / upper | Intervalle de confiance à 95 % |
reject | True = significatif ; False = non |
La double boucle d’exécution
Le pipeline complet est appliqué deux fois, à deux niveaux de granularité.
La fonction run_full_analysis() encapsule les 5 étapes. Le script l’appelle dans deux boucles :
Étape A — Scores ACP (4 analyses) : appliquée aux 4 scores globaux. « Le scénario influence-t-il la perception globale de chaque dimension ? »
Étape B — Items individuels (18 analyses) : appliquée aux 18 items bruts. « Sur quelle question précise le scénario fait-il bouger les réponses ? » L’Alignement global peut sembler stable, mais « L’agent serait honnête sur les limites des plats » pourrait diverger.
all_results = [] # ── ÉTAPE A : 4 construits globaux (scores ACP) ── for name, items in concepts.items(): res = run_full_analysis(pca_df, name, f"Concept Global : {name}") all_results.append(res) # ── ÉTAPE B : 18 items individuels ── for code, label in item_labels.items(): res = run_full_analysis(df_analysis, code, label) all_results.append(res)
Chaque appel renvoie un dictionnaire (F, p, η², ω², test utilisé, Levene p), collecté dans all_results pour le tableau de synthèse.
Synthèse finale automatisée
Un tableau récapitulatif et un verdict en langage clair.
summary_final = pd.DataFrame(all_results) print(summary_final[[ 'Variable', # Construit ou item 'Test_Appliqué', # "ANOVA" ou "Welch" 'F', # Statistique F 'p', # p-value 'Eta2', # Taille d'effet η² 'Omega2', # Taille d'effet ω² 'Levene_p' # p du test de Levene ]].to_string(index=False))
Ce tableau permet d’identifier d’un seul regard quelles variables ont un p < 0,05, quel test a été retenu, et la magnitude de chaque effet.
sig_found = summary_final[summary_final['p'] < 0.05] if sig_found.empty: print("Stabilité confirmée : même perception.") else: print(f"Divergence : {len(sig_found)} variable(s) significative(s).")
« Stabilité confirmée » — l’agent IA est perçu de la même manière quel que soit le scénario.
« Divergence détectée » — le scénario a modifié l’opinion. Les tests post-hoc identifient lesquels.
Pour chaque variable, un boxplot (médiane, quartiles, extrêmes) combiné à un swarmplot (chaque point = un participant) permet de voir la tendance centrale, la dispersion et la distribution réelle des réponses.
import seaborn as sns import matplotlib.pyplot as plt plt.figure(figsize=(7, 4)) sns.boxplot(x='GROUPE', y=target, data=data, hue='GROUPE', palette='Set2', legend=False) sns.swarmplot(x='GROUPE', y=target, data=data, color=".25", alpha=0.5, size=4) plt.title(f"Répartition : {label}") plt.show()
Code Python complet
Le script intégral, prêt à exécuter dans Google Colab ou Jupyter Notebook.
import pandas as pd
import numpy as np
import seaborn as sns
import matplotlib.pyplot as plt
import warnings
from sklearn.decomposition import PCA
from sklearn.preprocessing import StandardScaler
import statsmodels.api as sm
from statsmodels.formula.api import ols
from statsmodels.stats.anova import anova_lm
from statsmodels.stats.multicomp import pairwise_tukeyhsd
from scipy import stats
# 1. CONFIGURATION ET NETTOYAGE
warnings.simplefilter(action='ignore', category=FutureWarning)
warnings.simplefilter(action='ignore', category=UserWarning)
pd.options.mode.chained_assignment = None
# 2. CHARGEMENT ET RECODAGE
file_path = '/content/RC_AGENT.xlsx'
df = pd.read_excel(file_path, sheet_name='BASE')
df_analysis = df[df['GROUPE'].isin([1, 2, 3])].copy()
mapping_inverse = {1: 5, 2: 4, 3: 3, 4: 2, 5: 1}
df_analysis['CTRL3R_S1'] = df_analysis['CTRL3R_S1'].map(mapping_inverse)
item_labels = {
'ALIGN1_S1': "Agit dans mon meilleur intérêt",
'ALIGN2_S1': "Privilégiera mes intérêts vs restaurant",
'ALIGN3_S1': "Ne poussera pas à un choix avantageux resto",
'ALIGN4_S1': "Serait honnête sur les limites des plats",
'ALIGN5_S1': "S'assurera que la commande me convient",
'COMP1_S1': "Comprend mes préférences alimentaires",
'COMP2_S1': "Fait de bonnes suggestions de repas",
'COMP3_S1': "Est fiable pour gérer la commande",
'COMP4_S1': "Est compétent pour choisir un repas",
'CTRL1_S1': "Sentiment de garder le contrôle (préférences)",
'CTRL2_S1': "Contrôle via ajustement des préférences",
'CTRL3R_S1': "Perception de contrôle personnel (Inversé)",
'CTRL4_S1': "Facilité à refuser/annuler",
'CTRL5_S1': "Décision d'activer dépend de moi",
'INT1_S1': "Prévoit de laisser l'agent agir en mon nom",
'INT2_S1': "Compte laisser l'agent gérer la commande",
'INT3_S1': "Prêt à activer mode sans validation",
'INT4_S1': "Continuerait à utiliser ce mode à l'avenir"
}
concepts = {
'Alignement': ['ALIGN1_S1','ALIGN2_S1','ALIGN3_S1','ALIGN4_S1','ALIGN5_S1'],
'Compétence': ['COMP1_S1','COMP2_S1','COMP3_S1','COMP4_S1'],
'Contrôle': ['CTRL1_S1','CTRL2_S1','CTRL3R_S1','CTRL4_S1','CTRL5_S1'],
'Intention': ['INT1_S1','INT2_S1','INT3_S1','INT4_S1']
}
def calculate_eta_omega(ss_bet, ss_err, df_bet, ms_err):
ss_tot = ss_bet + ss_err
eta2 = ss_bet / ss_tot
omega2 = (ss_bet - (df_bet * ms_err)) / (ss_tot + ms_err)
return eta2, omega2
def welch_anova_test(data, target, group_col='GROUPE'):
k = data[group_col].nunique()
n = data.groupby(group_col)[target].count()
means = data.groupby(group_col)[target].mean()
vars_ = data.groupby(group_col)[target].var(ddof=1)
weights = n / vars_
sum_weights = weights.sum()
grand_mean_welch = (weights * means).sum() / sum_weights
num = (weights * (means - grand_mean_welch)**2).sum() / (k - 1)
lam = ((1 - weights / sum_weights)**2 / (n - 1)).sum()
den = 1 + (2 * (k - 2) / (k**2 - 1)) * lam
f_welch = num / den
df1 = k - 1
df2 = (k**2 - 1) / (3 * lam)
p_val = stats.f.sf(f_welch, df1, df2)
return f_welch, p_val
def run_full_analysis(data, target, label):
print(f"\n{'#'*70}\nANALYSE : {label}\n{'#'*70}")
desc = data.groupby('GROUPE')[target].agg(['mean','std','count','var']).round(3)
print("\n[1] DESCRIPTIFS :")
print(desc)
max_g = desc['mean'].idxmax()
min_g = desc['mean'].idxmin()
print(f"\n💡 Scénario {max_g} = meilleure moyenne ({desc.loc[max_g,'mean']}), "
f"Scénario {min_g} = plus faible ({desc.loc[min_g,'mean']}).")
g1 = data[data['GROUPE']==1][target]
g2 = data[data['GROUPE']==2][target]
g3 = data[data['GROUPE']==3][target]
levene_stat, levene_p = stats.levene(g1, g2, g3)
print(f"\n[2] LEVENE : F={levene_stat:.3f}, p={levene_p:.4f}")
if levene_p > 0.05:
print("→ Variances homogènes. ANOVA classique OK.")
else:
print("→ Variances hétérogènes. Bascule vers Welch.")
model = ols(f"{target} ~ C(GROUPE)", data=data).fit()
anova_tab = anova_lm(model, typ=2)
ss_bet = anova_tab.loc['C(GROUPE)','sum_sq']
ss_err = anova_tab.loc['Residual','sum_sq']
df_bet = anova_tab.loc['C(GROUPE)','df']
df_err = anova_tab.loc['Residual','df']
ms_bet = ss_bet / df_bet
ms_err = ss_err / df_err
f_stat = anova_tab.loc['C(GROUPE)','F']
p_val = anova_tab.loc['C(GROUPE)','PR(>F)']
eta2, omega2 = calculate_eta_omega(ss_bet, ss_err, df_bet, ms_err)
print(f"\n[3a] TABLE ANOVA :")
print(f"{'Source':<12} | {'SS':<10} | {'df':<4} | {'MS':<10} | {'F':<8} | {'Sig.':<8}")
print(f"{'Inter-Group':<12} | {ss_bet:<10.3f} | {df_bet:<4.0f} | {ms_bet:<10.3f} | {f_stat:<8.3f} | {p_val:<8.4f}")
print(f"{'Intra-Group':<12} | {ss_err:<10.3f} | {df_err:<4.0f} | {ms_err:<10.3f} |")
if levene_p < 0.05:
print("\n[3b] ⚠️ TEST DE WELCH :")
f_welch, p_welch = welch_anova_test(data, target, 'GROUPE')
print(f"F(Welch)={f_welch:.3f}, p={p_welch:.4f}")
reported_f, reported_p, test_used = f_welch, p_welch, "Welch"
else:
reported_f, reported_p, test_used = f_stat, p_val, "ANOVA"
if reported_p < 0.05:
print(f"\n💡 [{test_used}] p < 0,05 → Effet significatif.")
else:
print(f"\n💡 [{test_used}] p > 0,05 → Pas d'effet.")
print(f"\n[4] η²={eta2:.4f}, ω²={max(0,omega2):.4f}")
mag = "faible" if eta2<0.06 else "modérée" if eta2<0.14 else "forte"
print(f"→ Effet {mag} ({eta2*100:.1f}% de variance expliquée).")
if reported_p < 0.05:
print("\n[5] TUKEY HSD :")
if test_used == "Welch":
print("(Games-Howell serait préférable)")
tukey = pairwise_tukeyhsd(data[target], data['GROUPE'])
print(tukey)
else:
print("\n[5] Post-hoc non nécessaire.")
plt.figure(figsize=(7, 4))
sns.boxplot(x='GROUPE', y=target, data=data,
hue='GROUPE', palette='Set2', legend=False)
sns.swarmplot(x='GROUPE', y=target, data=data,
color=".25", alpha=0.5, size=4)
plt.title(f"Répartition : {label}")
plt.xlabel("Scénario"); plt.ylabel("Score")
plt.show()
return {'Variable': label, 'Test_Appliqué': test_used,
'F': round(reported_f,3), 'p': round(reported_p,4),
'Eta2': round(eta2,4), 'Omega2': round(max(0,omega2),4),
'Levene_p': round(levene_p,4)}
all_results = []
print("=" * 70)
print("ÉTAPE A : CONCEPTS GLOBAUX (ACP)")
print("=" * 70)
pca_df = pd.DataFrame({'GROUPE': df_analysis['GROUPE']})
for name, items in concepts.items():
scaler = StandardScaler()
pca = PCA(n_components=1)
pca_df[name] = pca.fit_transform(
scaler.fit_transform(
df_analysis[items].fillna(df_analysis[items].mean())
)).flatten()
all_results.append(run_full_analysis(pca_df, name, f"Global : {name}"))
print("\n\n" + "=" * 70)
print("ÉTAPE B : ITEMS INDIVIDUELS")
print("=" * 70)
for code, label in item_labels.items():
all_results.append(run_full_analysis(df_analysis, code, label))
summary_final = pd.DataFrame(all_results)
print("\n" + "=" * 100)
print("TABLEAU SYNTHÉTIQUE FINAL")
print("=" * 100)
print(summary_final[['Variable','Test_Appliqué','F','p',
'Eta2','Omega2','Levene_p']].to_string(index=False))
sig = summary_final[summary_final['p'] < 0.05]
if sig.empty:
print("\n→ Stabilité : aucune différence significative.")
else:
print(f"\n→ {len(sig)} variable(s) significative(s). Voir tests post-hoc.")